Ré sultats exp érimentaux
3.1. Introduction
Dans ce chapitre, nous allons soumettre notre
implémentation SVM avec l'algorithme SMO à deux types de tests:
les tests binaires appliquées aux paires des chiffres les plus
fréquemment confondus et les tests multi-classes Par l'approche
un-contre-tous. Différents noyaux serons utilisées avec
différents paramètres pour évaluer les performances des
SVMs .
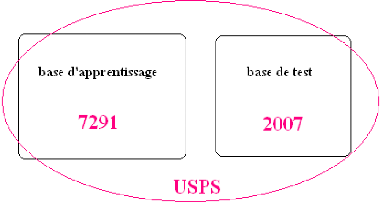
Figure 3.1.Représentation de la base USPS.
3.2. Critères d'évaluations
3.1.1. Base de données USPS (de
l'anglais«US postal Service »)
L'USPS est une base de données de chiffres manuscrits
extraits à partir d'enveloppes. La base de données contient 9298
images de chiffres manuscrits arabes dont 7291 images d'apprentissage servent
à construire le classifieur et 2007 images de test servent à
tester le classifieur et l'estimation de son taux d'erreur réel. Ces
images ont été saisies à partir d'images d'enveloppes
collectées au centre CEDAR à Buffalo (États Unis) [30].
Chaque image de chiffre est représentée par 16×16 pixels de
niveau de gris allant de 0 à 255 (Tableau 3.1). Il est connu que
l'ensemble de test d'USPS est plutôt difficile puisque l'erreur humaine
se situe autour de 2.5% [13].
Etiquettes
|
0
|
1
|
2
|
3
|
4
|
5
|
6
|
7
|
8
|
9
|
|

Images
Tableau 3.1. Échantillon représentant la
première dizaine d'images binarisées et
leurs
étiquettes dans la base de données USPS
Dans ce mémoire, nous nous restreignons à la
méthode SVM et aux images originales d'USPS. Une fraction de 500 images
a été extraire à partir de 7291 pour servir a
l'apprentissage et pour le test nous utilisons tous les prototypes (2007
image).
Pour évaluer la robustesse du classifieur, nous utilisons
la matrice de confusion pour estimer le taux de bonne reconnaissance.
3.1.2. Matrice de confusion
Dans la terminologie de l'apprentissage supervisé, la
matrice de confusion est un outil servant à mesurer la qualité
d'un système de classification. [29].Par exemple, si on considère
un système de classification dont le but est de classer des prototypes
en classe1 et en classe2, on va vouloir savoir combien de prototypes seront
faussement considérés comme du classe1 et combien de classe2 ne
seront pas identifiés comme tels. On va supposer qu'on a testé
notre classificateur avec 100 prototypes de classe 1 et 100 prototypes de
classe2. Ainsi la matrice suivante se lit comme suit :
· sur les 100 prototypes de classe 1, 95 seront
considérés comme tels et 5 seront pris pour du classe2 ;
· sur les 100 prototypes de classe2, 3 seront
interprétés comme classe1, et 97 seront reconnus en tant que
classe 1 ;
· sur les 98 prototypes que le système classe comme
classe1, 3 sont en fait du classe2 ;
· sur les 102 prototypes que le système classe comme
classe2, 5 sont en fait du classe 1.
· Taux global de bonne reconnaissance (TGBR) : (somme de
prototypes bien classées (diagonale)/somme totale) * 100
· Dans cet exemple= ((95+97)/200)*100=96.00
Référence
Classe 1 95 5
Classe 2
Décision
Classe 1
3
Classe 2
97
Figure 3.2.Exemple d'une matrice de confusion
· les colonnes correspondent aux décisions
correctes
· les lignes correspondent aux décisions
données par le classifieur.
Cette notion peut bien sûr s'étendre à un
nombre quelconque de classes. Un système de classification sera d'autant
meilleur que sa matrice de confusion s'approchera de la matrice diagonale.
3.3. Apprentissage des SVMs
3.3.1. Réglage des paramètres
Nous avons utilisé pour l'apprentissage binaire et
multiclasse les paramètres suivants :
3.3.1.1. Paramètre de régularisation C
La valeur du paramètre C est un hyper-paramètre
qui régit la performance du SVM. Ce paramètre sert à fixer
le compromis entre la minimisation de l'erreur d'apprentissage et la
maximisation de la marge. En pratique, le comportement du SVM est sensible
à la valeur de C uniquement si les données d'apprentissage ne
sont pas séparables. Dans ce cas, il existe des valeurs critiques qui
peuvent compromettre la performance du classifieur. Une très grande
valeur de C (quelques milliers) peut faire que la fonction objective
minimisée par le SVM ne soit plus convexe et empêcherait sa
convergence. Une très faible valeur de C tend à diminuer la
capacité du classifieur [20].
Dans ce travail, après quelques expériences, le
paramètre C a été fixé à 100 car il offre
les meilleures performances.
3.3.1.2 .Réglage des seuils de Tolérance et
å (=eps) :
L'algorithme SMO est basé sur
l'évaluation des conditions de KKT. Quand tous les multiplieurs
vérifient ces conditions, l'algorithme s'arrête. En pratique ces
conditions sont vérifiées à une erreur près
å . Platt [21] a mentionné dans son article que
å est typiquement choisi dans l'intervalle 10-2 et
10-3.
La maximisation de la marge doit être
tolérée de l'ordre :10%, 0.1%..etc
Dans notre cas nous avons fixé å , et la
tolérance a 1 0-3 .
3.3.2. Choix du noyau
Quatre noyaux ont été utilisés dans notre
travail :
· Polynomial
· RBF (Radial Basis Function)
· Distance négative
· KMOD : (de l'anglais «Kernel with Moderate
Decreasing») 3.4. Classification binaire
3.4.1. Choix des pairs de classes
Dans cette expérimentation, nous voulons
expérimenter la performance des SVMs pour séparer deux classes
les plus fréquemment confondus.Ces classes correspondant aux paires
(9,4), (5,6) et (7,1).
3.4.2. Evaluations
Pour évaluer l'influence du paramètre de chaque
noyau sur la qualité de la classification, nous avons calculé le
taux de bonne classification pour chaque paire de classes .Les résultats
sont présentés dans les tableaux suivants :
p=1
|
classe 9
|
classe4
|
classe 9
|
94.91
|
5.09
|
classe 4
|
3.5
|
96.5
|
|
a =3
|
classe 9
|
classe4
|
classe 9
|
94.91
|
5.08
|
classe 4
|
3.5
|
96.5
|
|
y = 0.2
|
classe 9
|
classe4
|
classe 9
|
96.04
|
3.95
|
classe 4
|
3
|
97
|
|
|
p=2
|
classe 9
|
classe4
|
|
classe 9
|
95.48
|
4.52
|
|
classe 4
|
4
|
96
|
(a)
a=10
|
classe 9
|
classe4
|
classe 9
|
96.04
|
3.95
|
classe 4
|
4
|
96
|
|
(b)
|
y=0.1
|
classe 9
|
classe4
|
|
classe 9
|
96.61
|
3.38
|
|
classe 4
|
4.5
|
95.50
|
(c)
|
p=3
|
classe 9
|
classe4
|
|
classe 9
|
96.04
|
3.95
|
|
classe 4
|
3.5
|
96.5
|
|
a =25
|
classe 9
|
classe4
|
|
classe 9
|
94.91
|
5.08
|
|
classe 4
|
3.5
|
96.5
|
|
y = 0.05
|
classe 9
|
classe4
|
|
classe 9
|
96.04
|
3.95
|
|
classe 4
|
4.5
|
95.5
|
|
a =6
et
y=0.2
|
classe 9
|
classe4
|
|
classe 9
|
95.48
|
4.51
|
|
classe 4
|
2.5
|
97.5
|
|
a =6
et
y=0.5
|
classe 9
|
classe4
|
|
classe 9
|
96.04
|
3.95
|
|
classe 4
|
3.50
|
96.50
|
(d)
|
Noyau
|
RBF
|
polynomial
|
Distance négative
|
KMOD
|
|
|
|
|
|
|
p=3
|
|
|
|
a=6
|
a=6
|
|
classe
|
a=3
|
a=10
|
a=25
|
p=1
|
p=2
|
|
y=0.2
|
y=0.1
|
y=0.05
|
et
|
et
|
|
|
|
|
|
|
|
|
|
|
y=0.5
|
y=0.2
|
|
9
|
94.91
|
96.04
|
94.91
|
94.91
|
95.48
|
96.04
|
96.04
|
96.61
|
96.04
|
96.04
|
95.48
|
|
4
|
96.50
|
96.00
|
96.50
|
96.50
|
96.00
|
96.50
|
97.00
|
95.50
|
95.50
|
96.50
|
97.50
|
|
TGBR
|
95.75
|
96.02
|
95.75
|
95.75
|
95.75
|
95.75
|
96.55
|
96.02
|
95.75
|
96.28
|
96.55
|
Tableau 3.2.Matrices de confusion pour les paires de classes (9
,4) pour chaque type de noyau (a) Polynomial (b) RBF (c) Distance
négative (d) KMOD
|
p=1
|
classe 5
|
classe6
|
|
classe 5
|
98.12
|
1.87
|
|
classe 6
|
5.29
|
94.70
|
|
a =3
|
classe 5
|
classe6
|
|
classe 5
|
98.75
|
1.25
|
|
classe 6
|
4.70
|
95.29
|
|
y = 0.2
|
classe 5
|
classe6
|
|
classe 5
|
98.75
|
1.25
|
|
classe 6
|
4.70
|
95.29
|
|
p=2
|
classe 5
|
classe6
|
|
classe 5
|
98.12
|
1.87
|
|
classe 6
|
4.70
|
95.29
|
(a)
a=10
|
classe 5
|
classe6
|
classe 5
|
98.12
|
1.87
|
classe 6
|
4.12
|
95.88
|
|
(b)
|
y=0.1
|
classe 5
|
classe6
|
|
classe 5
|
98.12
|
1.87
|
|
classe 6
|
5.29
|
94.70
|
(c)
|
p=3
|
classe 5
|
classe6
|
|
classe 5
|
99.37
|
0.62
|
|
classe 6
|
7.05
|
92.94
|
|
a =25
|
classe 5
|
classe6
|
|
classe 5
|
98.12
|
1.87
|
|
classe 6
|
4.7
|
95.29
|
|
y = 0.05
|
classe 5
|
classe6
|
|
classe 5
|
98.12
|
1.87
|
|
classe 6
|
4.11
|
95.88
|
|
a =6
et
y=0.2
|
classe 5
|
classe6
|
|
classe 5
|
98.75
|
1.25
|
|
classe 6
|
3.52
|
96.47
|
|
a =6
et
y=0.5
|
classe 5
|
classe6
|
|
classe 5
|
98.75
|
1.25
|
|
classe 6
|
3.52
|
96.47
|
|
p=1
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
2.27
|
97.72
|
|
p=2
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
2.65
|
97.34
|
(a)
|
p=3
|
classe 7
|
classe 1
|
|
classe 7
|
100
|
0
|
|
classe 1
|
2.65
|
97.34
|
(d)
|
Noyau
|
RBF
|
polynomial
|
Distance négative
|
KMOD
|
|
|
|
|
|
|
p=3
|
|
|
|
a=6
|
a=6
|
|
classe
|
a =3
|
a =10
|
a =25
|
p=1
|
p=2
|
|
y = 0.2
|
y = 0.1
|
y = 0.05
|
et
|
et
|
|
|
|
|
|
|
|
|
|
|
y=0.5
|
y=0.2
|
|
5
|
98.75
|
98.12
|
98.12
|
98.12
|
98.12
|
99.37
|
98.75
|
98.12
|
98.12
|
98.75
|
98.75
|
|
6
|
95.29
|
95.88
|
95.29
|
94.70
|
95.29
|
92.94
|
95.29
|
94.70
|
95.88
|
96.47
|
96.47
|
|
TGBR
|
96.96
|
96.96
|
96.66
|
96.36
|
96.66
|
96.06
|
96.96
|
96.36
|
96.96
|
97.57
|
97.57
|
Tableau 3.3.Matrices de confusion pour les paires de classes (5
,6) pour chaque type de noyau (a) Polynomial (b) RBF (c) Distance
négative (d) KMOD
|
a=3
|
classe 7
|
classe1
|
|
classe 7
|
100
|
0
|
|
classe 1
|
3.40
|
96.59
|
|
a=10
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
2.66
|
97.34
|
|
a=25
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
2.65
|
97.34
|
|
y=0.2
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
3.40
|
96.59
|
(b)
|
y=0.1
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
3.40
|
96.59
|
(c)
|
y=0.05
|
classe 7
|
classe1
|
|
classe 7
|
99.31
|
0.68
|
|
classe 1
|
3.40
|
96.59
|
|
a =6
et
y=0.2
|
classe 7
|
classe1
|
|
classe 7
|
100
|
0
|
|
classe 1
|
3.40
|
96.59
|
|
a =6
et
|
classe 7
|
classe1
|
|
y=0.5
|
|
|
|
classe 7
|
100
|
0
|
|
classe 1
|
3.40
|
96.59
|
(d)
|
Noyau
|
RBF
|
polynomial
|
Distance négative
|
KMOD
|
|
|
|
|
|
|
p=3
|
|
|
|
a=6
|
a=6
|
|
classe
|
a =3
|
a =10
|
a =25
|
p=1
|
p=2
|
|
y = 0.2
|
y = 0.1
|
y = 0.05
|
et
|
et
|
|
|
|
|
|
|
|
|
|
|
y=0.5
|
y=0.2
|
|
7
|
100
|
99.31
|
99.31
|
99.31
|
99.31
|
100
|
99.31
|
99.31
|
99.31
|
100
|
100
|
|
1
|
96.59
|
97.34
|
97.34
|
97.72
|
97.34
|
97.34
|
96.59
|
96.59
|
96.59
|
96.59
|
96.59
|
|
TGBR
|
97.81
|
98.05
|
98.05
|
98.29
|
98.05
|
98.29
|
97.56
|
97.56
|
97.56
|
97.81
|
97.81
|
Tableau 3 .4.Matrices de confusion pour les paires de classes (7
, 1) pour chaque type de noyau (a) Polynomial (b) RBF (c) Distance
négative (d) KMOD
3.4.3. Comparaison des résultats et
discussions
|
Noyau
|
RBF
|
Polynomial
|
Distance négative
|
KMOD
|
|
pairs
|
a=3
|
a=10
|
a=25
|
p=1
|
p=2
|
p=3
|
y=0.2
|
y=0.1
|
y=0.05
|
a=6
|
a=6
|
|
|
|
|
|
|
|
|
|
|
et
|
et
|
|
|
|
|
|
|
|
|
|
|
y=0.5
|
y=0.2
|
|
(9,4)
|
95.75
|
96.02
|
95.75
|
95.75
|
95.75
|
95.75
|
96.55
|
96.02
|
95.75
|
96.28
|
96.55
|
|
(5,6)
|
96.96
|
96.96
|
96.66
|
96.36
|
96.66
|
96.06
|
96.96
|
96.36
|
96.96
|
97.57
|
97.57
|
|
(7,1)
|
97.81
|
98.05
|
98.05
|
98.29
|
98.05
|
98.29
|
97.56
|
97.56
|
97.56
|
97.81
|
97.81
|
Tableau 3.5.Taux global de bonne reconnaissance pour les trois
paires de classes (9,4), (7,1) et (5,6).
D'une manière générale, les
résultats obtenus sont sensiblement similaires en termes de bonne
classification .Cependant, l'analyse comparative montre que le choix du noyau
dépend des paires de classes et des paramètres utilisés.
En effet nous avons constaté que les noyaux KMOD et Distance
négative ont les mêmes performances pour la paire (9,4) .Tandis
que le noyau Polynomial fournit le meilleurs taux pour la paire(7,1) .Pour la
paire (5,6) le noyau KMOD fournit le meilleurs taux de bonne reconnaissance.
3.5. Classification multi classe
3.5.1. Evaluations
Dans cette section, nous évaluons la classification
multi-classe en utilisant l'approche un contre tous pour les différents
noyaux et différents paramètres des noyaux.
Les matrices de confusion sont reportées dans les tableaux
suivants :
|
ó =3
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
92.75
|
0
|
2.50
|
0.27
|
1.39
|
0.55
|
0.83
|
0.27
|
1.39
|
0
|
|
un
|
0
|
93.18
|
0.75
|
0
|
3.40
|
0
|
1.51
|
0
|
1.13
|
0
|
|
deux
|
1.01
|
0
|
84.34
|
2.02
|
3.53
|
1.51
|
1.01
|
0.50
|
6.06
|
0
|
|
trois
|
1.20
|
0
|
3.61
|
80.12
|
0.60
|
7.83
|
0
|
0
|
6.02
|
0.60
|
|
quatre
|
0
|
0.50
|
3.00
|
0
|
85.50
|
0
|
1.00
|
0.50
|
3.00
|
6.50
|
|
cinq
|
2.50
|
0
|
1.25
|
5.00
|
1.87
|
82.50
|
0
|
0
|
5.00
|
1.87
|
|
six
|
2.35
|
0
|
4.70
|
0
|
1.76
|
3.52
|
86.47
|
0
|
1.17
|
0
|
|
sept
|
0
|
0
|
2.04
|
0.68
|
6.12
|
0
|
0
|
80.27
|
4.08
|
6.80
|
|
huit
|
1.80
|
0
|
1.80
|
0
|
1.20
|
3.61
|
0
|
0
|
90.96
|
0.60
|
|
neuf
|
0
|
0
|
0.56
|
0
|
3.38
|
0
|
0
|
0.56
|
2.25
|
93.22
|
|
TGBR
|
|
87.84
|
Tableau 3 .6.Matrice de confusion de la classification multi
classe pour le noyau RBF (ó =3)
|
ó =10
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
89.69
|
0
|
5.01
|
1.39
|
1.39
|
1.11
|
0.27
|
0
|
0.27
|
0.83
|
|
un
|
0
|
95.07
|
0.37
|
0
|
3.40
|
0
|
0.37
|
0
|
0.37
|
0.37
|
|
deux
|
1.51
|
0
|
80.30
|
3.53
|
7.07
|
2.02
|
0.50
|
0.50
|
4.54
|
0
|
|
trois
|
1.20
|
0
|
3.01
|
83.73
|
1.20
|
3.61
|
0
|
0
|
3.61
|
3.61
|
|
quatre
|
0.50
|
0.50
|
2.00
|
0
|
87.00
|
0.50
|
0.50
|
1.00
|
3.00
|
5.00
|
|
cinq
|
2.50
|
0
|
3.12
|
10.62
|
3.12
|
73.75
|
0.62
|
1.25
|
3.75
|
1.25
|
|
six
|
2.35
|
0
|
7.05
|
0
|
4.11
|
6.47
|
77.64
|
0.58
|
1.17
|
0.58
|
|
sept
|
0.68
|
0
|
2.72
|
2.72
|
6.12
|
0
|
0
|
79.59
|
1.36
|
6.80
|
|
huit
|
3.01
|
1.20
|
2.40
|
3.61
|
5.42
|
4.81
|
0
|
1.80
|
74.09
|
3.61
|
|
neuf
|
0
|
0
|
0.56
|
0
|
6.21
|
0.56
|
0
|
1.12
|
2.25
|
89.26
|
|
TGBR
|
|
84.35
|
Tableau 3 .7.Matrice de confusion de la classification multi
classe le noyau RBF (ó = 10)
|
ó =25
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
90.25
|
0
|
3.89
|
1.94
|
1.39
|
0.27
|
0.83
|
0
|
1.11
|
0.27
|
|
un
|
0
|
95.83
|
0
|
0.75
|
1.89
|
0
|
1.13
|
0
|
0.37
|
0
|
|
deux
|
2.02
|
0
|
78.78
|
7.07
|
6.56
|
1.01
|
0.50
|
0.50
|
3.53
|
0
|
|
trois
|
2.40
|
0
|
2.40
|
86.14
|
1.20
|
4.81
|
0
|
0
|
2.40
|
0.60
|
|
quatre
|
0
|
1.5
|
3
|
0
|
86.00
|
0
|
1.00
|
0
|
4.50
|
4.00
|
|
cinq
|
1.87
|
0.62
|
5.00
|
12.50
|
1.87
|
72.50
|
0.62
|
0
|
3.75
|
1.25
|
|
six
|
2.35
|
0
|
7.64
|
0
|
3.52
|
3.52
|
81.17
|
0
|
1.76
|
0
|
|
sept
|
0.68
|
0.68
|
2.04
|
2.72
|
6.80
|
0
|
0
|
74.82
|
7.72
|
9.52
|
|
huit
|
3.61
|
1.80
|
3.01
|
3.61
|
4.21
|
2.40
|
0
|
1.20
|
78.91
|
1.20
|
|
neuf
|
0
|
1.12
|
1.12
|
1.12
|
5.64
|
1.12
|
0
|
0.56
|
2.25
|
87.00
|
|
TGBR
|
|
84.55
|
Tableau 3.8.Matrice de confusion de la classification multi
classe le noyau RBF (ó =25)
|
P=1
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
89.41
|
0
|
3.89
|
0.55
|
1.11
|
2.78
|
1.11
|
0.55
|
0.55
|
0
|
|
un
|
0
|
95.07
|
0
|
0
|
2.27
|
0
|
1.51
|
0.37
|
0.75
|
0
|
|
deux
|
1.01
|
0
|
72.72
|
2.52
|
8.08
|
2.52
|
4.04
|
3.03
|
6.06
|
0
|
|
trois
|
1.80
|
0
|
3.01
|
68.07
|
0.60
|
13.25
|
0.60
|
1.20
|
9.03
|
2.40
|
|
quatre
|
0.50
|
1.00
|
1.00
|
0
|
81.50
|
3.50
|
1.50
|
2.50
|
4.50
|
4.00
|
|
cinq
|
3.75
|
0
|
0
|
5
|
1.25
|
83.75
|
0
|
2.5
|
2.5
|
1.25
|
|
six
|
2.35
|
0
|
2.35
|
0
|
2.94
|
7.64
|
82.35
|
0.58
|
1.76
|
0
|
|
sept
|
1.36
|
0
|
1.36
|
0.68
|
3.40
|
1.36
|
0
|
87.07
|
1.36
|
3.40
|
|
huit
|
4.21
|
0
|
0.60
|
0.60
|
3.61
|
9.63
|
0
|
2.40
|
77.10
|
1.80
|
|
neuf
|
0
|
0.56
|
1.12
|
0
|
5.64
|
2.25
|
0
|
5.08
|
6.77
|
78.53
|
|
TGBR
|
|
82.76
|
Tableau 3.9.Matrice de confusion de la classification multi
classe pour le noyau Polynomial (p=1)
|
P=2
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
89.97
|
0
|
3.06
|
0.83
|
1.67
|
2.78
|
1.11
|
0
|
0.55
|
0
|
|
un
|
0
|
95.45
|
0
|
0
|
3.03
|
0
|
1.13
|
0
|
0.37
|
0
|
|
deux
|
1.51
|
0
|
73.23
|
3.03
|
7.57
|
2.52
|
4.04
|
1.01
|
7.07
|
0
|
|
trois
|
3.61
|
0
|
2.40
|
73.49
|
0.60
|
10.24
|
0
|
0
|
8.43
|
1.20
|
|
quatre
|
0.50
|
1.00
|
1.50
|
0
|
83.50
|
1.50
|
1.50
|
0
|
3.00
|
7.50
|
|
cinq
|
3.12
|
0
|
0.62
|
5.00
|
1.87
|
85.00
|
0
|
0.62
|
2.50
|
1.25
|
|
six
|
0.58
|
0
|
2.35
|
0
|
3.52
|
8.82
|
82.35
|
0
|
2.35
|
0
|
|
sept
|
0
|
0
|
2.04
|
0.68
|
4.76
|
1.36
|
0
|
78.23
|
2.04
|
10.88
|
|
huit
|
3.61
|
1.20
|
0
|
1.20
|
2.40
|
9.63
|
0
|
1.20
|
78.91
|
1.80
|
|
neuf
|
0
|
0.56
|
0.56
|
0
|
5.08
|
1.69
|
0
|
0.56
|
3.95
|
87.57
|
|
TGBR
|
|
84.01
|
Tableau 3.1 0.Matrice de confusion de la classification multi
classe pour le noyau Polynomial (p=2)
|
P=3
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
92.47
|
0
|
2.50
|
1.11
|
1.39
|
0.55
|
0.83
|
0.27
|
0
|
0.83
|
|
un
|
0
|
95.83
|
0
|
0
|
2.65
|
0
|
1.13
|
0
|
0.37
|
0
|
|
deux
|
2.02
|
0
|
77.27
|
3.53
|
6.56
|
1.51
|
4.04
|
1.51
|
3.53
|
0
|
|
trois
|
2.40
|
0
|
2.40
|
80.12
|
0.60
|
6.02
|
0.60
|
0
|
4.21
|
3.61
|
|
quatre
|
1.00
|
1.00
|
2.00
|
0
|
82.50
|
1.00
|
1.50
|
1.00
|
2.00
|
8.00
|
|
cinq
|
1.87
|
0
|
1.25
|
9.37
|
1.87
|
79.37
|
0.62
|
1.25
|
1.87
|
2.5
|
|
six
|
2.35
|
0
|
2.35
|
0
|
4.70
|
3.52
|
85.88
|
0.58
|
0.58
|
0
|
|
sept
|
0
|
0
|
2.04
|
0.68
|
4.08
|
1.36
|
0
|
82.99
|
0.68
|
8.16
|
|
huit
|
4.81
|
0.60
|
1.80
|
1.80
|
4.21
|
7.83
|
0.60
|
2.40
|
71.08
|
4.81
|
|
neuf
|
0
|
0.56
|
0.56
|
0
|
3.38
|
1.12
|
0
|
0.56
|
2.25
|
91.52
|
|
TGBR
|
|
85.25
|
Tableau 3.11 .Matrice de confusion de la classification multi
classe pour le noyau Polynomial (p=3)
|
ã=0.2
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
93.31
|
0
|
3.34
|
0.27
|
1.11
|
0.27
|
0.83
|
0.83
|
0
|
0
|
|
un
|
0
|
95.83
|
0
|
0
|
2.27
|
0
|
1.51
|
0.37
|
0
|
0
|
|
deux
|
1.51
|
0
|
86.86
|
2.52
|
3.53
|
1.51
|
1.01
|
2.02
|
1.01
|
0
|
|
trois
|
1.80
|
0
|
3.61
|
86.74
|
0.60
|
5.42
|
0.60
|
0
|
0
|
1.20
|
|
quatre
|
0
|
1.50
|
5.00
|
0
|
85.50
|
0
|
1.00
|
2.50
|
0
|
4.50
|
|
cinq
|
1.87
|
0
|
3.12
|
10.62
|
1.87
|
78.75
|
0.62
|
1.87
|
0
|
1.25
|
|
six
|
2.94
|
0
|
5.29
|
0
|
2.35
|
2.94
|
86.47
|
0
|
0
|
0
|
|
sept
|
0.68
|
0.68
|
2.72
|
0.68
|
3.40
|
0
|
0
|
88.43
|
0
|
3.40
|
|
huit
|
2.40
|
1.80
|
6.62
|
8.43
|
7.83
|
8.43
|
0
|
3.61
|
56.02
|
4.81
|
|
neuf
|
0.56
|
0.56
|
1.12
|
0.56
|
5.64
|
0.56
|
0
|
3.38
|
6.77
|
78.53
|
|
TGBR
|
|
86.00
|
Tableau 3.1 2.Matrice de confusion de la classification multi
classe pour le noyau KMOD ã =0.2 et ó =6
|
ã =0.5
|
zéro
|
Un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
93.87
|
0
|
1.67
|
0.55
|
1.11
|
0.55
|
0.55
|
0.55
|
0
|
1.11
|
|
un
|
0
|
93.81
|
0
|
1.13
|
1.89
|
0
|
2.27
|
0.37
|
0
|
1.13
|
|
deux
|
2.52
|
0
|
78.28
|
5.05
|
5.55
|
2.02
|
1.51
|
2.52
|
2.02
|
0.50
|
|
trois
|
1.20
|
0
|
2.40
|
87.34
|
0.60
|
6.02
|
0
|
0
|
0
|
2.40
|
|
quatre
|
0.50
|
0.50
|
2.50
|
0
|
81.50
|
1.00
|
1.00
|
2
|
0
|
10.00
|
|
cinq
|
2.50
|
0
|
1.25
|
8.75
|
1.87
|
80.62
|
0
|
1.87
|
0.62
|
2.50
|
|
six
|
3.52
|
0
|
3.52
|
0
|
2.35
|
4.70
|
85.88
|
0
|
0
|
0
|
|
sept
|
0
|
0
|
0.68
|
0.68
|
3.40
|
0
|
0
|
89.79
|
0
|
5.44
|
|
huit
|
4.81
|
0
|
0.60
|
7.22
|
4.21
|
8.43
|
0
|
3.01
|
63.25
|
8.43
|
|
neuf
|
0.56
|
0
|
0.56
|
0
|
2.25
|
0.56
|
0
|
2.25
|
0
|
93.78
|
|
TGBR
|
|
85.89
|
Tableau 3.13 .Matrice de confusion de la classification multi
classe pour le noyau KMOD ã =0.5 et ó =6
|
ã=0.2
|
zéro
|
un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
90.25
|
0
|
1.94
|
0.83
|
1.39
|
3.06
|
1.67
|
0
|
0.83
|
0
|
|
un
|
0
|
93.93
|
0
|
0
|
2.27
|
0
|
1.51
|
0
|
1.51
|
0.75
|
|
deux
|
2.02
|
0
|
68.68
|
3.03
|
7.57
|
2.02
|
3.53
|
1.01
|
12.12
|
0
|
|
trois
|
2.40
|
0
|
1.20
|
75.90
|
1.20
|
5.42
|
0.60
|
0.60
|
10.24
|
2.40
|
|
quatre
|
1.00
|
0.50
|
0.50
|
0
|
84.00
|
0
|
3.00
|
1.00
|
5.00
|
5.00
|
|
cinq
|
3.12
|
0
|
1.25
|
10
|
3.12
|
74.37
|
0
|
1.25
|
5.00
|
1.87
|
|
six
|
0.58
|
0
|
1.17
|
0
|
2.94
|
7.64
|
85.29
|
0
|
2.35
|
0
|
|
sept
|
0.68
|
0
|
1.36
|
1.36
|
4.76
|
0
|
0
|
82.31
|
4.08
|
5.44
|
|
huit
|
3.01
|
0
|
0
|
1.80
|
0.60
|
3.61
|
0
|
0
|
90.36
|
0.60
|
|
neuf
|
0
|
0.56
|
0
|
0
|
3.95
|
1.12
|
0
|
0.56
|
8.47
|
85.31
|
|
TGBR
|
|
84.10
|
Tableau 3.14.Matrice de confusion de la classification multi
classe pour le noyau Distance négativeã =0.2
|
ã=0.1
|
zéro
|
un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
91.36
|
0
|
3.62
|
0.55
|
1.11
|
0.27
|
2.22
|
0
|
0.27
|
0.55
|
|
un
|
0
|
95.45
|
0
|
0
|
2.27
|
0
|
1.51
|
0
|
0
|
0.75
|
|
deux
|
1.51
|
0
|
77.27
|
4.04
|
6.06
|
1.51
|
4.04
|
2.02
|
3.03
|
0.50
|
|
trois
|
2.40
|
0
|
1.20
|
77.10
|
2.40
|
7.22
|
0.60
|
1.20
|
3.01
|
4.81
|
|
quatre
|
0.50
|
0.50
|
1.50
|
0
|
82.00
|
0
|
4.00
|
0.50
|
1.00
|
10.00
|
|
cinq
|
4.37
|
0
|
2.50
|
12.50
|
3.12
|
71.25
|
0.62
|
0.62
|
2.50
|
2.50
|
|
six
|
1.17
|
0
|
2.35
|
0
|
2.94
|
5.29
|
87.64
|
0
|
0.58
|
0
|
|
sept
|
0
|
0
|
1.36
|
0
|
4.08
|
0
|
0
|
87.07
|
0.68
|
6.80
|
|
huit
|
5.42
|
1.80
|
3.61
|
1.80
|
4.21
|
7.83
|
0
|
1.20
|
71.08
|
3.01
|
|
neuf
|
0
|
0
|
0.56
|
0
|
3.38
|
0.56
|
0
|
1.12
|
1.12
|
93.22
|
|
TGBR
|
|
84.65
|
Tableau 3. 15.Matrice de confusion de la classification multi
classe pour le noyau Distance négative ã=0.1
|
ã =0.05
|
zéro
|
un
|
deux
|
trois
|
quatre
|
cinq
|
six
|
sept
|
huit
|
neuf
|
|
|
zéro
|
92.75
|
0
|
1.39
|
0.83
|
1.11
|
0.27
|
2.22
|
0.55
|
0.27
|
0.55
|
|
un
|
0
|
93.93
|
0
|
0.75
|
1.51
|
0
|
3.03
|
0
|
0
|
0.75
|
|
deux
|
2.52
|
0
|
69.19
|
7.57
|
7.07
|
1.01
|
6.06
|
3.03
|
3.03
|
0.50
|
|
trois
|
1.80
|
0
|
1.20
|
86.74
|
0.60
|
3.61
|
0.60
|
1.80
|
0.60
|
3.01
|
|
quatre
|
1.00
|
0.50
|
1.00
|
0
|
84.00
|
0
|
3.00
|
1.50
|
0.50
|
8.50
|
|
cinq
|
4.37
|
0
|
1.25
|
13.12
|
2.50
|
75.00
|
0
|
1.25
|
0
|
2.50
|
|
six
|
2.35
|
0
|
0
|
0.58
|
2.94
|
5.29
|
88.82
|
0
|
0
|
0
|
|
sept
|
0.68
|
0
|
1.36
|
0.68
|
4.08
|
0
|
0
|
89.11
|
0
|
4.08
|
|
huit
|
4.81
|
0.60
|
0.60
|
7.83
|
7.22
|
7.22
|
0.60
|
1.20
|
66.26
|
3.61
|
|
neuf
|
0.56
|
0
|
0.56
|
0
|
5.64
|
1.12
|
0
|
1.69
|
0.56
|
89.83
|
|
TGBR
|
|
84.75
|
Tableau 3.16.Matrice de confusion de la classification multi
classe pour le noyau Distance négative ã=0.05
3.5.2. Comparaison des résultats et
discussions
|
noyau
|
RBF
|
polynomial
|
Distance négative
|
KMOD
|
|
classe
|
|
|
|
|
|
|
|
|
|
ã = 0.5
|
ã = 0.2
|
|
ó=3
|
ó=10
|
ó=25
|
p=1
|
p=2
|
p=3
|
ã=0.2
|
ã=0.1
|
ã=0.05
|
ó=6
|
ó=6
|
|
0
|
92.75
|
89.69
|
90.25
|
89.41
|
89.97
|
92.47
|
90.25
|
91.36
|
92.75
|
93.87
|
93.31
|
|
1
|
93.18
|
95.07
|
95.83
|
95.07
|
95.45
|
95.83
|
93.93
|
95.45
|
93.93
|
93.18
|
95.83
|
|
2
|
84.34
|
80.30
|
78.78
|
72.72
|
73.23
|
77.27
|
68.68
|
77.27
|
69.19
|
78.28
|
86.86
|
|
3
|
80.12
|
83.73
|
86.14
|
68.07
|
73.49
|
80.12
|
75.90
|
77.10
|
86.74
|
87.34
|
86.74
|
|
4
|
85.50
|
87.00
|
86.00
|
81.50
|
83.50
|
82.50
|
84.00
|
82.00
|
84.00
|
81.50
|
85.50
|
|
5
|
82.50
|
73.75
|
72.50
|
83.75
|
85.00
|
79.37
|
74.37
|
71.25
|
75.00
|
80.62
|
78.75
|
|
6
|
86.47
|
77.64
|
81.17
|
82.35
|
82.35
|
85.88
|
85.29
|
87.64
|
88.82
|
85.88
|
86.47
|
|
7
|
80.27
|
79.59
|
74.82
|
87.07
|
78.23
|
82.99
|
82.31
|
87.07
|
89.11
|
89.79
|
88.43
|
|
8
|
90.96
|
74.09
|
78.91
|
77.10
|
78.91
|
71.08
|
90.36
|
71.08
|
66.26
|
63.25
|
56.02
|
|
9
|
93.22
|
89.26
|
87.00
|
78.53
|
87.57
|
91.52
|
85.31
|
93.22
|
89.83
|
93.78
|
87.57
|
|
TGBR
|
87.84
|
84.35
|
84.55
|
82.76
|
84.01
|
85.25
|
84.10
|
84.65
|
84.75
|
85.89
|
86.00
|
Tableau 3. 17.Résumé des résultats pour la
classification multi classe
Globalement, les taux de bonne reconnaissance sont
sensiblement similaires. Cependant, nous constatons que le choix du noyau et
ses paramètres influent sur le taux de bonne de reconnaissance .Le noyau
RBF pour ó =3 semble fournir les meilleurs taux de bonne de
reconnaissance comparativement aux autres noyaux. L'examen du taux de bonne de
reconnaissance pour chaque classe montre qu'il n'existe pas un noyau plus
favorable .En fait les résultats obtenus dépendent des
classes.
Nous présentons dans les figures suivantes le taux de
bonne de reconnaissance pour chaque classe et pour différentes valeurs
du paramètre du noyau.
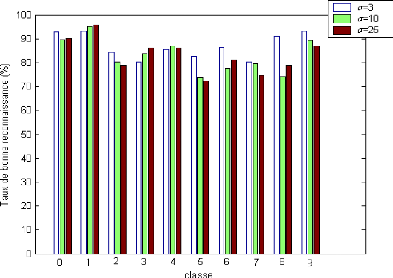
Figure 3.3.Taux de bonne reconnaissance (%) pour chaque classe
pour différents valeurs du
paramètre du noyau RBF.
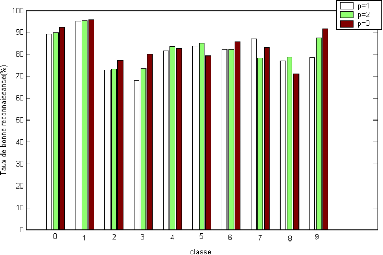
Figure 3.4.Taux de bonne reconnaissance (%) pour chaque classe
pour différents valeurs du
paramètre du noyau Polynomial.
Chapitre 3 Résultats expérimentaux
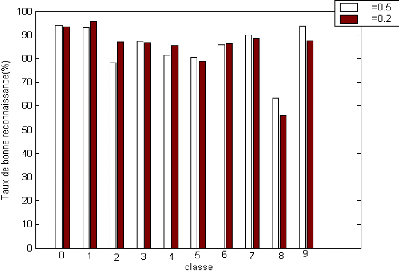
Y Y
Figure 3.5.Taux de bonne reconnaissance (%) pour chaque classe
pour différents valeurs du
paramètre du noyau KMOD (a
=6)
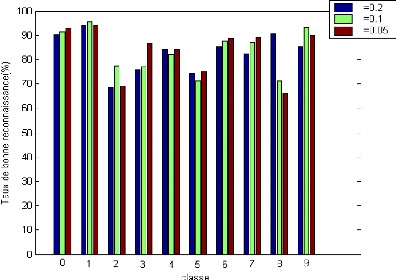
Y Y Y
Figure 3.6.Taux de bonne reconnaissance (%) pour chaque classe
pour différents valeurs du
paramètre du noyau Distance
négative
3.6. Comparaison classification binaire et
multi-classe
L'analyse comparative entre la classification binaire et la
classification multi-classe montre que le taux de bonne reconnaissance pour la
classification binaire est meilleur quelques soit le noyau utilisé
comparativement à la classification multi-classe. Cela peut se justifier
par le fait que le classifieur SVM a beaucoup plus de difficultés
à séparer une classe des autres classes comparativement à
la classification binaire.
3.7. Présentation de la plateforme
Nous présentons dans cette section la plate forme de
reconnaissance de chiffres manuscrits implémentés sous
environnement Matlab .Les différentes fonctions
implémentés sont décrits dans les sous- sections
suivants.
3.7.1. Fenêtre principale
La fenêtre principale est composée (voir figure3.7)
de trois menus :
· Fichier,
· Apprentissage
· Test.
Figure 3.7. Fenêtre principale
3.7.2 Menu
3.7.2.1. Sélection des fichiers (voir figure3.8)
Le menu Fichier contient trois rubriques :
> Ouvrir la base d 'apprentissage : permet de
sélectionner le fichier sur lequel porte l'apprentissage des SVMs .La
sélection porte sur (voir figure3.9) :
· Le nom du fichier de données
· Le nom du fichier des classes
· Nombres d'images
· Hauteur de l'image
· Largeur de l'image
> Ouvrir la base de test : permet d'ouvrir la base
de test et les classes correspondantes
>
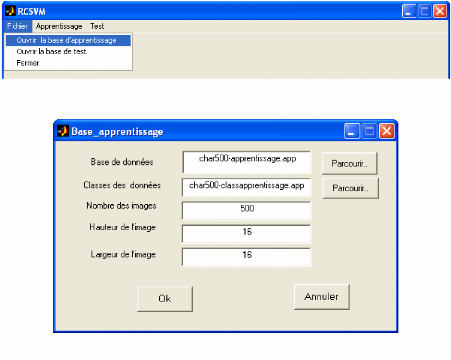
Figure 3.8. Rubriques de menu Fichier
Figure 3.9. Exemple de chargement de la base d'apprentissage.
Fermer : sert à quitter la plateforme.
3.7.2.2. Sélection des paramètres pour
l'apprentissage (voir figure3.10) Le menu Apprentissage
contient deux rubriques :
> Svm multiclasse : permet de faire la classification
multi-classe par le choix du noyau et le réglage de ses
paramètres (figure3.11)
> Svm biclasse : permet de faire la classification bi-classe
entre deux classes choisis en sélectionnant le noyau et ses
paramètres (figure3.12).
Figure 3.10. Rubriques de menu Apprentissage.
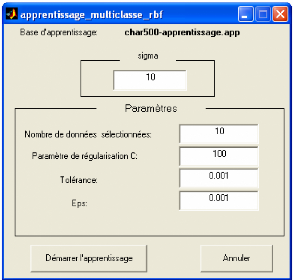
Figure 3.11. Exemple de choix de noyau et les paramètres
pour la classification multiclasse
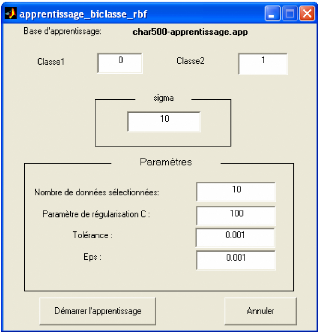
Figure 3.12. Exemple de choix de noyau et réglage des
paramètres avec possibilité de
sélectionner deux
classes pour la classification biclasse.
3.7.2.3. Evaluation de la classification (voir figure
3.13)
Le menu Test contient deux rubriques :
> Test binaire : permet d'afficher la matrice de confusion et
la précision globale pour la classification biclasse.
> Test multi : permet pour la classification multiclasse :
+ De calculer la matrice de confusion et la précision
globale (voir figure 3.14).
+ D'afficher le taux de bonne reconnaissance de
déférentes classes avec leur graphe (voir figure 3.15).
+ D'afficher le taux de bonne reconnaissance de
déférentes classes sous forme d'une matrice de confusion et
graphique avec la précision globale. (voir figure 3.16).
+ De récapituler tous les résultats obtenus avec
les paramètres utilisés et d'afficher le temps d'apprentissage et
le temps de test (voir figure 3.17).
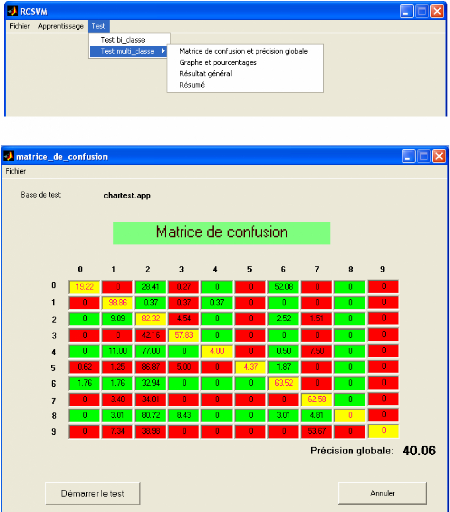
Figure 3.13. Rubriques de menu Test.
Figure 3.14.Matrice de confusion avec précision
globale.
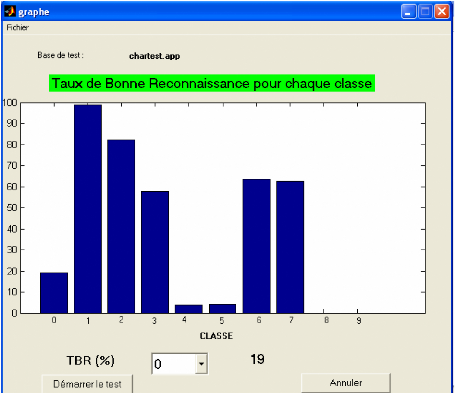
Figure 3.15. Taux de bonne reconnaissance pour chaque classe
représenté sous forme
graphique
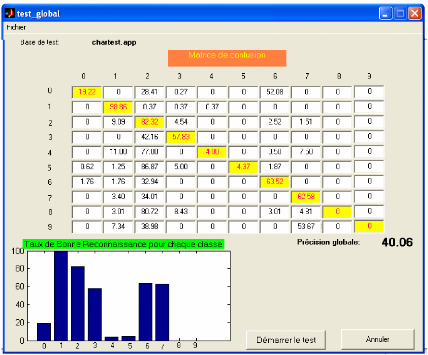
Figure 3.16. Taux de bonne reconnaissance pour
déférentes classes représenté sous forme
d'une
matrice de confusion et graphique.
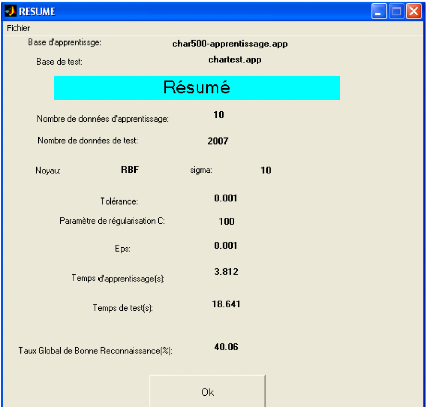
Figure 3.1 7.Résumé des résultats
3.8. Conclusion
Ce chapitre a été consacré à
l'évaluation du classifieur SVM pour la reconnaissance des chiffres
manuscrits. Les résultats obtenus montrent que la qualité de la
reconnaissance dépend du choix du noyau et du réglage de ses
paramètres.
Par ailleurs, nous avons pu constater que la séparation
bi-classe permet de séparer plus facilement deux classes que de
séparer une classe des autres classes.
| 

