ADN et marqueurs génétiques
iii
deux brins et chaque brin est constitué de
l'enchaînement précis de quatre éléments de base,
les nucléotides (cf Figure 1) (Boichard et al., 1998). Ces
nucléotides diffèrent selon la base azotée qu'ils
contiennent : l'adénine notée A, la guanine (G), la thymine (T)
et la cytosine (C). Les successions des nucléotides sur les deux brins
sont complémentaires (la base C est complémentaire à la
base G et la base T est complémentaire à la base A). Cette
succession des nucléotides constitue la séquence de l'ADN. Un
marqueur génétique se
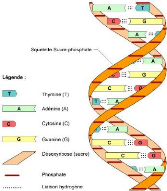
FIG. 1 - Structure d'une molécule d'ADN
trouve à des endroits précis du
génôme et est dans la suite synonyme de locus marqueur; un locus
marqueur est un locus polymorphe dont le génotype renseigne sur le
génotype d'un ou de plusieurs locus voisin(s) (De Vienne, 1998). Un
marqueur génétique de qualité "idéale" est :
1. polymorphe, c'est à dire qu'il possède
plusieurs allèles;
2. co-dominant, c'est à dire un locus pour lequel tous
les allèles présents peuvent être simplement déduits
de l'observation du phénotype; l'hétérozygote peut
être distingué de l'homozygote au locus;
3. non-épistasique, c'est à dire qu'il n'y a pas
d'interaction inter-locus; le génotype en un locus est
indépendant du génotype aux autres locus;
4. neutre, une substitution des allèles au locus marqueur
n'a pas d'autres effets phénotypiques que ceux qui permettent de
déterminer son gé-
notype; un marqueur neutre révèle directement les
modifications géné-
tiques qu'elles se traduisent ou non par
une modification phénotypique;
5. insensible au milieu, le génotype peut être
déduit du phénotype indépendamment du milieu.
Les plus courants des marqueurs génétiques sont
les marqueurs biochimiques, les marqueurs morphologiques et les marqueurs
moléculaires. Mais le plus souvent, ce sont les marqueurs
moléculaires qui ont, pour la plupart, toutes les qualités
citées ci-dessus, au moins lorsque les techniques appropriées
sont mises en oeuvre (De Vienne, 1998). Les marqueurs moléculaires
permettent une caractérisation du génome de manière
fiable, spécifique et rapide. Ainsi, nous nous intéresserons
essentiellement, dans la suite, aux marqueurs moléculaires. Les
marqueurs microsatellites ou SSR (Simple Sequence Repeats) sont des
séquences constituées de répétition en tandem
(toujours dans le même sens) d'un à quatre nucléotides
répétés de 10 à 20 fois en moyenne. Par exemple,
(A)Th , (TC)Th, (TAT)Th et (GATA)Th
avec ii le nombre de répétitions, sont des marqueurs
microsatellites couramment observés. Très nombreux et bien
répartis sur le génome, les microsatellites se
caractérisent par un important polymorphisme dû à la
variation du nombre de répétitions selon les allèles
(Boichard et al., 1998). Il s'agit ainsi d'un polymorphisme du nombre
d'unités de répétitions et l'importance de ce
polymorphisme constitue l'intérêt des marqueurs microsatellites.
Les microsatellites sont des marqueurs dits multialléliques, c'est
à dire qu'ils permettent de révéler une série de
plusieurs allèles par locus. Les locus ainsi mis en évidence sont
le plus souvent codominants et les deux allèles homologues sont
observables chez un individu hétérozygote. Pour que le marqueur
microsatellite puisse être repéré sans
ambiguïté , il doit être entouré de part et d'autre
par des séquences flanquantes uniques, appelées amorces,
permettant d'identifier le locus. En effet, bien qu'un microsatellite
donné ne soit pas spécifique d'un locus, les séquences
flanquantes par contre le sont et une paire d'amorces spécifiques de ces
régions flanquantes n'amplifiera que ce microsatellite. Ainsi, puisque
les séquences des régions flanquantes sont
généralement identiques pour les individus d'une même
espèce, un locus microsatellite particulier peut souvent être
identifié par ses séquences flanquantes (Selkoe et Toonen,
2006).
La mise en évidence du polymorphisme du marqueur est
réalisée par l'amplification par PCR (Polymerase Chain Reaction)
de la séquence entourant le microsatellite puis par
électrophorèse sur gel d'acrylamide dont la haute
résolution permet de distinguer des allèles dont la taille
diffère de deux bases seulement (Boichard et al., 1998). La PCR,
réaction de polymérisation en chaîne, est un
procédé de biologie moléculaire permettant d'amplifier in
vitro une zone spécifique de l'ADN (la séquence cible) comprise
entre deux
v
amorces connues. Cette technique permet, grâce a
l'utilisation de l'enzyme polymérase qui résiste a de très
hautes températures (thermo-résistante) et des amorces
spécifiques, de multiplier par un facteur 2 le fragment d'ADN cible a
chaque cycle et de le rendre ainsi facilement détectable après un
certain nombre de cycles. Chaque cycle est constitué des trois
étapes suivantes effectuées chacune a une température bien
précise :
1. dénaturation; la dénaturation de l'ADN a
94° consiste a dissocier les deux brins d'ADN (rupture des liaisons
hydrogènes entre les deux brins);
2. hybridation; la température est abaissée
rapidement durant 45s a une température définie selon le type
d'amorce et ainsi les amorces hybrident sur leur brin complémentaire;
3. élongation; une hausse rapide de la
température a 72° durant 1 mn permet a l'enzyme polymérase
(la Taq polymérase) d'ajouter des nucléotides aux amorces
hybridées en respectant la complémentarité des bases.
| 


